
订购NovaSeq X系列
将先进的化学、光学和信息学技术相结合,实现了超凡的速度和数据质量、出色的通量和可扩展性。
全面的新一代测序(NGS)检测,靶向与实体瘤相关的170个基因。
分析时间
手动操作时间
起始量
包含NextSeq 500/550 v2测序试剂(货号 OP-101-1003和20018621)已停产。TruSight Tumor 170 Kit with NextSeq v2.5 Reagents(货号20028821)是推荐的替代产品。TruSight Tumor 170 Kit Plus Watson for Genomics(货号20018622)也已停产。如果您需要该分析,请继续直接与IBM合作。因美纳始终致力于为您提供高质量的支持和服务。
TruSight Tumor 170是一种NGS检测方法,可评估170个与常见实体瘤相关的基因。
使用单个样本的DNA和RNA评估多种变异类型,从而最大限度地提高单检测效率,节省宝贵的组织、时间和资源。专家精选的基于证据的内容为研究人员提供了最有可能在肿瘤发生中发挥作用的变异的全面覆盖。
DNA和RNA文库可同时制备、测序和分析,实现多种类型的体细胞变异的高效评估。
使用BaseSpace Sequence Hub上的TruSight Tumor 170应用程序进行测序数据分析和管理。基于Docker的软件上提供本地二级分析。
| Cancer type | Solid Tumor |
|---|---|
| Method | Target Enrichment, Targeted RNA Sequencing, Targeted DNA Sequencing |
| Specialized sample types | Low-Input Samples, FFPE Tissue |
| Variant class | Gene fusions, Single nucleotide variants (SNVs), Insertions-deletions (indels), Copy number variants (CNVs), Structural variants, Somatic variants |
| 内容说明 | 探针富集了170个基因的完整编码序列。可检测151个基因中的单核苷酸变异、小插入和缺失,59个基因中的扩增,以及55个基因中的融合和剪接变异。 |
| 分析时间 | 约2天 |
| 多重分析 | 使用两个标签集,DNA可重达32重,RNA可重达16重 |
| 手动操作时间 | 约10.5小时 |
| 技术 | Illumina测序 |
| 核酸类型 | DNA, RNA |
| 物种 | 人 |
| 系统 | NextSeq 550 Desktop Sequencer, NextSeq 500 Desktop Sequencer, HiSeq 2500 |
| 自动化详情 | 探索可用的自动化方法 |
| 说明 | 利用DNA和RNA的变异检出信息,在实体瘤中开展全面的体细胞变异检测研究。 |
| 起始量 | 40 ng DNA和/或RNA |
需要使用NextSeq 500/550 v2.5试剂和Pierian解读软件。
TruSight Tumor 170可高效全面覆盖单个FFPE样本中RNA和DNA中的癌症相关变异(小变异、扩增、剪接变异和融合)。
| 仪器 | Recommended number of samples | Read length |
|---|---|---|
| NextSeq 550 System | Samples per run (high output): 16 (8 DNA + 8 RNA), 10 if DNA only, 16 if RNA only |
2 × 101 bp(建议最大) |
| TruSight Tumor 170 | TruSight Oncology 500 High-Throughput(大样本量方案) | TruSight Oncology 500 | TruSight Oncology 500 ctDNA v2 | |
|---|---|---|---|---|
| Cancer type | Solid Tumor | Pan-Cancer, Solid Tumor | Pan-Cancer, Solid Tumor | Pan-Cancer, Solid Tumor |
| Method | Target Enrichment, Targeted RNA Sequencing, Targeted DNA Sequencing | Target Enrichment, Targeted RNA Sequencing, Targeted DNA Sequencing | Target Enrichment, Targeted RNA Sequencing, Targeted DNA Sequencing | Target Enrichment, Targeted DNA Sequencing |
| Specialized sample types | Low-Input Samples, FFPE Tissue | FFPE Tissue | FFPE Tissue | Circulating Tumor DNA, Blood |
| Variant class | Gene fusions, Single nucleotide variants (SNVs), Insertions-deletions (indels), Copy number variants (CNVs), Structural variants, Somatic variants | Gene fusions, Transcript variants, Single nucleotide variants (SNVs), Insertions-deletions (indels), Copy number variants (CNVs), Novel transcripts, Structural variants, Somatic variants | Gene fusions, Transcript variants, Single nucleotide variants (SNVs), Insertions-deletions (indels), Copy number variants (CNVs), Loss of heterozygosity (LOH), Somatic variants, Novel transcripts, Single nucleotide polymorphisms (SNPs), Structural variants | Single nucleotide variants (SNVs), Insertions-deletions (indels), Copy number variants (CNVs) |
| 内容说明 | 探针富集了170个基因的完整编码序列。可检测151个基因中的单核苷酸变异、小插入和缺失,59个基因中的扩增,以及55个基因中的融合和剪接变异。 |
靶向测序523个目标基因的DNA和55个基因的RNA,panel大小总计为1.94 Mb。包括MSI和TMB测量。 |
对来自523个基因的DNA和来自55个基因的RNA进行靶向测序,总panel大小为1.94 Mb。包括MSI和TMB测量。 可选的TruSight Oncology 500 HRD试剂盒(日本不可用)内容包括约25K SNP的覆盖度,可通过Myriad Genetics支持的全面基因组不稳定性评分(LOH+TAI+LST)评估同源重组缺陷。 |
靶向选择523个基因(完整编码序列),panel总共1.94 Mb。 • 免疫肿瘤学生物标志物覆盖度:TMB和MSI • 指南覆盖范围:广泛覆盖多种实体瘤的重要指南 • 临床试验覆盖范围:600多项临床试验(基于Pierian临床知识库,截至2023年2月) |
| 分析时间 | 约2天 |
从样本到结果需要4-5天 |
从样本到结果需要4-5天 |
从纯化核酸到变异报告,<4天 |
| 多重分析 | 使用两个标签集,DNA可重达32重,RNA可重达16重 |
多达16重(SP流动槽)、32重(S1流动槽)、72重(S2流动槽)和192重(S4流动槽) |
多达8重 | 在S2上可进行8重分析,在S4上可进行24重分析(使用Xp-4 Lane工作流程,最多16个标签) |
| 手动操作时间 | 约10.5小时 |
自动化工作流程约2.5小时。 手动工作流程约10.5小时。 |
自动化工作流程约2.5小时。 手动工作流程约10.5小时。 |
文库制备和富集约2.5小时 |
| 技术 | Illumina测序 | Illumina测序 | Illumina测序 | Illumina测序 |
| 核酸类型 | DNA, RNA | DNA, RNA | DNA, RNA | DNA |
| 物种 | 人 | 人 | 人 | 人 |
| 系统 | NextSeq 550 Desktop Sequencer, NextSeq 500 Desktop Sequencer, HiSeq 2500 | NovaSeq 6000Dx in Research Mode, NovaSeq 6000 System | NextSeq 550 Desktop Sequencer, NextSeq 550Dx in Research Mode, NextSeq 500 Desktop Sequencer | NovaSeq 6000 System |
| 自动化详情 | 探索可用的自动化方法 | 探索可用的自动化方法 | 探索可用的自动化方法 | |
| 说明 | 利用DNA和RNA的变异检出信息,在实体瘤中开展全面的体细胞变异检测研究。 |
一种高通量的综合NGS检测方法,利用NovaSeq 6000系统或NovaSeq 6000Dx仪器(研究模式),通过简化的工作流程鉴定指南和>1K临床试验中的关键生物标志物。覆盖免疫肿瘤学生物标志物MSI和TMB。 |
该检测能够对FFPE组织进行全面的基因组分析,并在NextSeq 550系统或NextSeq 550Dx仪器(研究模式)上运行,一次最多可批量处理8个样本。 |
通过液体活检样本(血浆中的ctDNA)的全景基因组图谱分析,提供了一种非侵入性方法,用于癌症研究应用的实体瘤图谱分析。这种液体活检方法利用微创样本采集方法来补充基于组织的CGP,提供了有关肿瘤内和肿瘤间异质性的见解。 |
| 起始量 | 40 ng DNA和/或RNA |
40 ng DNA和/或40–80 ng RNA |
40 ng DNA和/或40 ng RNA |
20 ng cfDNA(4 mL血浆) |
寻找符合您需求的测序文库制备试剂盒或芯片。按方法、种类等筛选。比较、分享和订购试剂盒。
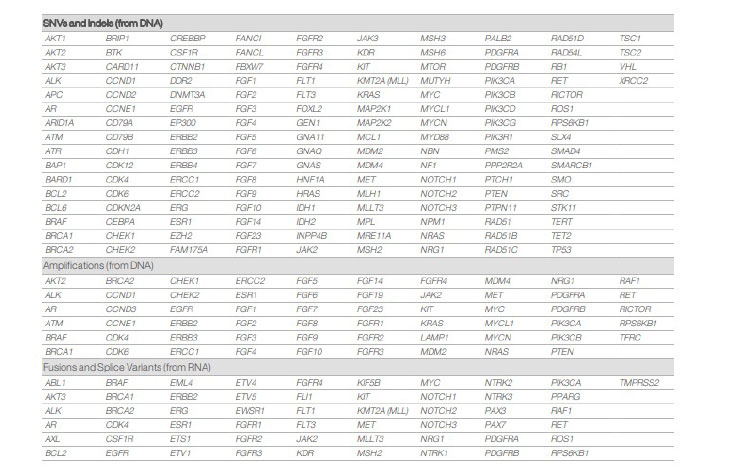

TruSight tumor 170靶向170个基因中当前RefSeq数据库1的所有编码外显子。这些基因和基因区域覆盖55个基因融合和剪接变异体、148个SNV和插入缺失以及59个扩增。
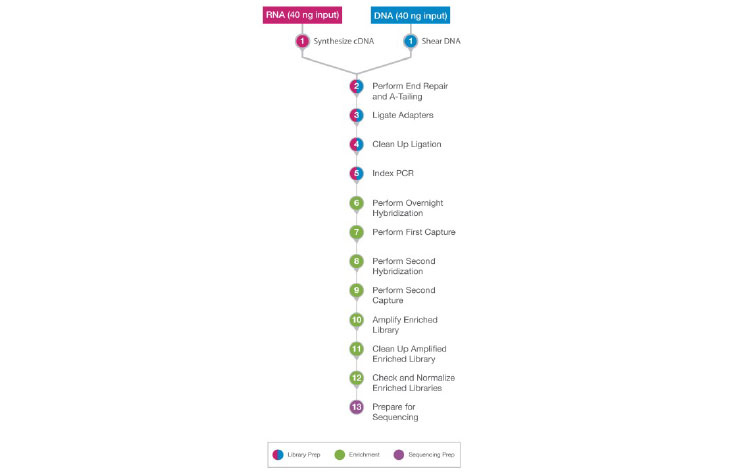

在cDNA合成步骤(RNA)和剪切步骤(DNA)之后,DNA和RNA样本遵循相同的工作流程。
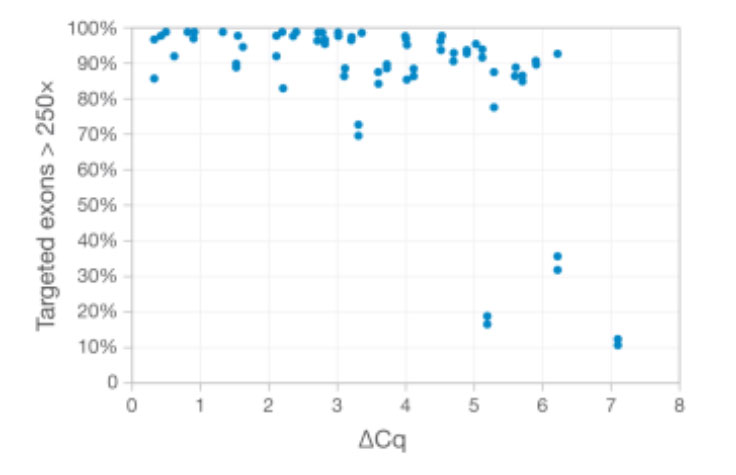

使用TruSight Tumor 170提取并评估来自不同质量FFPE样本的DNA,并在NextSeq 500系统上测序。使用qPCR评估样本质量,以测量DNA扩增潜力。ΔCq值表示每个DNA样本的循环阈值(Ct)减去DNA标准品的Ct值。
了解单次检测如何同时检测DNA和RNA,以最大限度地提高单个FFPE样本的产出。
TruSight Tumor 170 Kit (24 Samples)
OP-101-1004
该试剂盒包含文库制备试剂、富集试剂和测序耗材,能对FFPE样本的170个基因进行实体瘤分析。
List Price:
Discounts:
TruSight Tumor 170 Kit, With NextSeq v2.5 Reagents (24 Samples)
20028821
包含文库制备试剂、富集试剂和测序耗材,能对FFPE样本的170个基因进行实体瘤分析。
List Price:
Discounts:
显示 /
产品
数量
Unit Price
产品
货号
数量
单价
在文库制备和富集过程中,DNA和RNA样本在样本剪切(DNA)和cDNA合成(RNA)后会经历相同的工作流程。这样可以同时处理DNA和RNA样本。然后,可以在同一个测序运行中对DNA和RNA文库进行测序。
TruSight Tumor 170试剂盒中不包含提取试剂。QIAGEN AllPrep DNA/RNA FFPE Kit(货号80234)已证明与本检测的其他提取方法相比,核酸产量高。QIAGEN AllPrep DNA/RNA FFPE Kit包含RNA提取过程中的DNase I消化步骤。您可以自行决定选择其他市售提取试剂盒。
TruSight Tumor 170的性能已在NextSeq 500和NextSeq 550系统以及HiSeq 2500系统上以快速运行模式进行了验证。
Illumina建议添加至少40 ng DNA或RNA。对于高度降解的样本,最多可使用120 ng DNA和85 ng RNA来提高检测性能。
覆盖度可能因样本质量和多重分析水平而异。请查看TruSight Tumor 170应用程序为每次分析生成的DNA_SampleMetricsReport.txt和RNA_SampleMetricsReport.txt文件。此报告包含一个指标,表示覆盖度>100×的碱基百分比。使用8个高质量DNA和8个高质量RNA样本(16个文库)进行的测序运行表明,在100倍覆盖度下,碱基≥99%。
使用BaseSpace Sequence Hub云环境中提供的TruSight Tumor 170应用程序或本地Docker应用程序来分析TruSight Tumor 170文库。
参考文献:
1. O'Leary NA, Wright MW, Brister JR, et al. NCBI的参考序列(RefSeq)数据库:当前状态、分类扩展和功能注释。核酸 Res. 2016;44(D1):D733-45。
doi:10.1093/nar/gkv1189
获取有关我们产品和服务的信息,或获得有关我们技术问题的答案。
Your email address is never shared with third parties.